Herhaalde metingen
| Auteur | dr. ir. N van Geloven | |
| Co-Auteur | prof. dr. A.H. Zwinderman | |
| auteurschap op deze site | ||
Wat zijn herhaalde metingen?
Herhaalde metingen zijn meerdere metingen van dezelfde variabele bij dezelfde persoon, patient, proefdier, of algemeen geformuleerd, dezelfde observationele eenheid. Voorbeelden:
- herhaling in de tijd: als patienten herhaaldelijk in een follow-up periode worden gemeten (of: voor en na een behandeling);
- meerdere locaties: metingen op meerdere locaties in het lichaam van dezelfde persoon (linker en rechter oog, meerdere coupes in een biopt, meerdere slices in een MRI beeld);
- meerdere condities: als dezelfde patient onder twee of meer verschillende condities (bijv. behandelingen) wordt gemeten, bijvoorbeeld bij een cross-over studie;
- herhalingen tbv nauwkeurigheid: als een meting een grote variatie binnen een persoon heeft (of een grote meetfout) dan kan het zinvol zijn om een aantal aparte metingen te doen;
- multilevel structuren: als metingen bij meerdere personen gedaan zijn die onderdeel uitmaken van dezelfde groep. Bijvoorbeeld patienten die dezelfde huisarts hebben, waarbij de interventie per huisartspraktijk is uitgevoerd. Het klassieke voorbeeld hier zijn leerlingen die dezelfde docent hebben en docenten die weer bij eenzelfde school horen.
Waarom kun je bij herhaalde metingen geen standaard regressiemodel gebruiken?
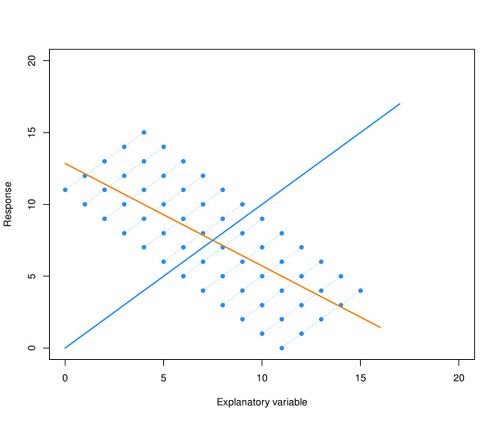
Bij een standaard regressiemodel wordt aangenomen dat alle metingen onafhankelijk van elkaar zijn. Bij herhaalde metingen is het waarschijnlijk dat twee metingen van dezelfde persoon meer op elkaar lijken dan twee metingen van verschillende personen. Als dat zo is, dan zijn de metingen binnen dezelfde persoon niet onafhankelijk. Als bij herhaalde metingen geen rekening wordt gehouden met deze afhankelijkheid, dan zijn i.h.a. de standaard fouten en de p-waardes (onterecht!) te klein. Bovendien kan de uitkomst van de regressie-analyse volkomen fout zijn, zoals geïllustreerd in het plaatje dat hieronder staat. In deze figuur worden de observaties van 12 personen getoond en elke persoon laat een duidelijk stijgende trend zien. Als de afhankelijkheid van de waarnemingen genegeerd wordt, dan is de best passende regressielijn door de totale puntenwolk de oranje dalende lijn en deze geeft geen correcte weergave van de trend per patiënt.
Welke analyses zijn er mogelijk voor herhaalde metingen?
- Simpele methodes: Soms kunnen herhaalde metingen samengevat worden in een enkele relevante maat. Je kunt bijvoorbeeld de meting van slechts een tijdpunt gebruiken, de verandering tussen twee meetpunten gebruiken, een samenvattende maat zoals het gemiddelde of de area under the curve uitrekenen, of de tijd tot het bereiken van een bepaald level analyseren in een survival analyse.
- Geavanceerde methodes: Methodes die wel herhaalde metingen aankunnen zijn o.a. mixed effects modellen, repeated measures ANOVA en generalized estimating equations (GEE).
De simpele methodes gebruiken maar een deel van de verzamelde informatie en dat levert vaak minder onderscheidingsvermogen (power) op. Repeated measurements ANOVA is een specifieke variant van mixed-models, maar is alleen beschikbaar voor continue normaal verdeelde afhankelijke variabelen, die op vaste en dezelfde tijdstippen zijn gemeten in alle patienten. Mixed-models en GEE-modellen zijn wat lastiger te specificeren, maar zijn flexibeler en zijn beschikbaar voor zowel continue normaal verdeelde afhankelijke variabelen, als voor bijv dichotome afhankelijke variabelen. Bovendien kunnen de mixed modellen ook omgaan met een zekere mate van missing values, namelijk wanneer de data missing at random zijn.
Repeated measures ANOVA
Repeated measurements analysis of variance (ANOVA) is een statistische methode om herhaalde metingen van een continue, normaal verdeelde afhankelijke variabele te analyseren. Deze methode is te gebruiken als de afhankelijke variabel op een beperkte aantal vaste tijdstippen is gemeten en waarbij alle patiënten op alle tijdstippen gemeten zijn.
Area under the curve
Wanneer er op meerdere tijdstippen metingen zijn van een patient, kun je die samenvatten in een "area under the curve". Hierbij bereken je per patient de oppervlakte onder de gemeten punten in de tijd. Deze samenvattende maat gebruik je vervolgens voor de analyse.
Hoe bereken ik met SPSS een area under the curve bij herhaalde metingen?
Ik wil graag van een bepaalde meting in de tijd, op verschillende tijdstippen gemeten, de 'area under the curve' bepalen. Ik kom er met SPSS niet uit. Ik moet er nl een stuk of 300 bepalen... heeft u nog een advies?
Je kunt de volgende syntax gebruiken, deze rekent per patient een area under the curve uit. Bovenaan het document staat beschreven hoe je de variabelen in SPSS moet hebben staan.
Hoe kan ik data van 4 experimenten combineren?
De experimenten die ik verricht, heb ik in 4 sessies opgesplitst, aangezien het niet behapbaar was alle samples in een keer te verwerken. Nu blijkt dat de vergelijkingsgroepen (verschillende diagnoses) binnen elke serie toch wel erg klein zijn en vraag ik me af of en hoe ik de data van de 4 series zou kunnen combineren.
Wat wel gebruikt wordt bij zulk soort settings is het toepassen van een factor correctie. Zie ook de referentie naar de paper van Ruijter [1] onderaan op deze pagina. Je kunt ook binnen een statistisch model een correctie voor de 'clustering' binnen sessies meenemen, bijvoorbeeld door een mixed of glm-repeated analyse te doen. Je beschouwt de experimenten dan als 'herhaalde metingen' binnen een sessie.
Referenties
-
Ruijter JM, Thygesen HH, Schoneveld OJ, Das AT, Berkhout B, Lamers WH, Factor correction as a tool to eliminate between-session variation in replicate experiments: application to molecular biology and retrovirology, Retrovirology. 2006 Jan 6;3:2. [1]
-
Gueorguieva R, Krystal JH. Move Over ANOVA: Progress in Analyzing Repeated-Measures Data and Its Reflection in Papers Published in the Archives of General Psychiatry. Arch Gen Psychiatry. 2004 Mar;61(3):310-7. [1]
-
BT, Analyzing Longitudinal Data With the Linear Mixed Models Procedure in SPSS. Eval Health Prof 2009 32: 207-228. [1]
Informatie op andere websites
- Deze post van Jonathan Bartlett over Odds ratios, collapsibility, marginal vs. conditional, GEE vs GLMMs geeft aan wat het verschil is tussen GEE en GLMM (mixed model) aanpak bij binaire uitkomsten.
- GEE newsletter van Cornell Statistical Consulting Unit, Cornell University.
- The analysis factor - The Repeated and Random Statements in Mixed Models for Repeated Measures info over het onderscheid tussen de repeated en de random statement in SPSS mixed.
- The analysis factor info over de verschillende aanpakken voor herhaalde metingen: repeated measurements anova, marginal model, mixed model.
- Robin Beaumont Heath Informatics course material Vrij te gebruiken cursusmateriaal over linear mixed models met uileg van specificatie in zowel SPSS als R, zie week 6 7 en 8. Inclusief bijbehorende Youtube instructiefilmpjes.
Sofwaretips
- GLLAMM Een familie functies (vrij te downloaden/attachen) in Stata, waarbij er opties zijn voor het modelleren van herhaaldelijk gemeten niet continue uitkomstmaten (dichotome, ordinale etc).
- SuperMix Een standalone programma geschikt voor het modelleren van herhaaldelijk gemeten niet continue uitkomstmaten (dichotome, ordinale etc).
Klaar met lezen? Je kunt naar het OVERZICHT van alle statistische onderwerpen op deze wiki gaan of naar de pagina KEUZE TOETS voor hulp bij het uitzoeken van een geschikte toets of analyse. Wil je meer leren over biostatistiek? Volg dan de AMC e-learning Practical Biostatistics. Vind je op deze pagina's iets dat niet klopt? Werkt een link niet? Of wil je bijdragen aan de wiki? Neem dan contact met ons op.
De wiki biostatistiek is een initiatief van de helpdesk statistiek van Amsterdam UMC, locatie AMC. Medewerkers van Amsterdam UMC, locatie AMC kunnen via intranet ondersteuning aanvragen. Ondersteuning aan studenten of derden is niet mogelijk.